GapBlasterは、ゲノムのアセンブリで得られたコンティグを用いて、NNNで繋がったスキャフォールドのクローズを支援するjavaのツール。GUIで動作する。アセンブリで得られたコンティグをblast+/legacy blast/mummerの新井面ツールでスキャホールドにアライメントして、NNNの配列に一致するだろうcontigを絞り込んでいる。論文の表5には、GAGE-Bのデータセットを使って、 Abyss、ABySS2、AllPaths-LG、Bambus2、MSR-CA、SGA、SOAPdenovo、VelvetのNNNが解消された割合がまとめられている。
マニュアル
https://sourceforge.net/projects/gapblaster2015/files/?source=navbar
インストール
依存
- mummer
- blast+
- legacy blast
ubuntu(Debian)ならapt-getで導入できる。
sudo apt-get install blast2
sudo apt-get install mummer
sudo apt-get install ncbi-blast+
本体はjavaの実行形式のバイナリで配布されている。
https://sourceforge.net/projects/gapblaster2015/
ラン
ターミナルでバイナリを実行すればGUIパネルが起動する。
java -jar GapBlaster_v1.1.2.jar
contigとscaffolds(NNN..を含む)を選択してRunを押す。
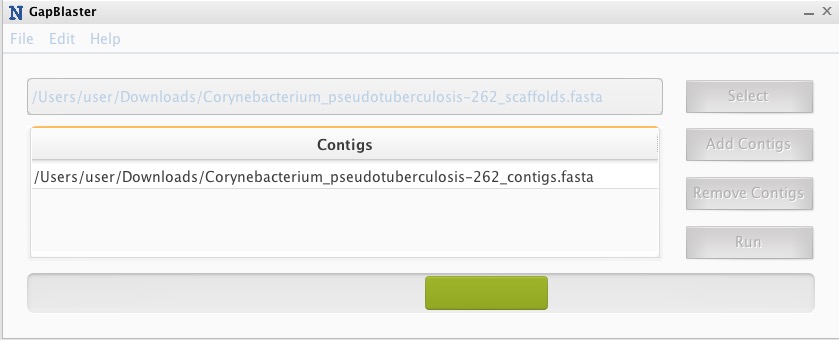
ランが終わると、アライメントされたscaffoldsとcontigの延期部分が表示される。また、NNNの解消を試みたscaffoldのFASTAファイルが自動出力される。
引用
GapBlaster—A Graphical Gap Filler for Prokaryote Genomes
Pablo H. C. G. de Sá , Fábio Miranda , Adonney Veras, Diego Magalhães de Melo, Siomar Soares, Kenny Pinheiro, Luis Guimarães, Vasco Azevedo, Artur Silva, Rommel T. J. Ramos
PLoS One. 2016 May 12;11(5):e0155327.