細菌ゲノムや古細菌ゲノムの完全シークエンスから単一の遺伝子配列とコンテキストを検索することは、ウェットベンチ生物学者にとっては気が遠くなるような作業である。既存のウェブベースのゲノムブラウザは、日常的に使用するには複雑すぎるか、原核生物ゲノムのサブセットしか提供していない。
菌類や古細菌の遺伝子の塩基配列やシンテニーをマウスを3回クリックするだけで閲覧できるWebサービス「BAGET 2.0 (Bacterial and Archaeal Gene Exploration Tool)」を開発した。ユーザーが提供したアノテーションされたゲノムも処理することができる。BAGET 2.0は毎日更新されるローカルデータベースに依存している。
BAGET 2.0は、Chrome、Firefox、Edge、Opera、Safariなどの現行ブラウザに対応しているほか、Internet Explorer 11をサポートしている。BAGET 2.0は https://archaea.i2bc.paris-saclay.fr/baget/ から自由にアクセスできる。
help
https://archaea.i2bc.paris-saclay.fr/baget/Home/Help#genome_selection
https://archaea.i2bc.paris-saclay.fr/baget/にアクセスする。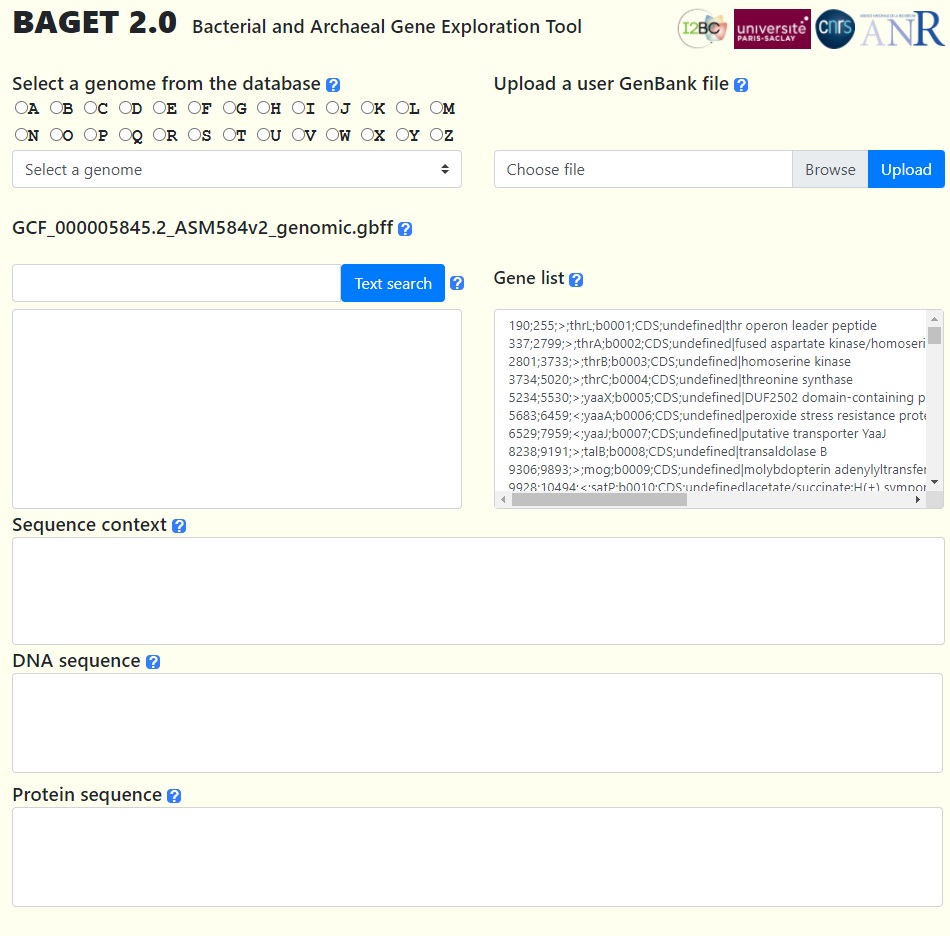
ゲノムを指定するか、ファイルをアップロードする。

ファイルをアップロードする場合、GenBankファイル(full)を指定する(DNA配列が含まれているGenBnak(ジェンバンク)ファイル)。NCBIからファイルをダウンロードする際には、アノテーションの下にDNA配列が追加されるように、GenBank (full)オプションにチェックをつける。

FTPサーバーからダウンロードするなら、gbff.gzファイルを選ぶ。
アップロードが完了するか、リストからゲノムが選ばれると、右のGene listウィンドウに認識された全ての遺伝子が表示される。

何かの遺伝子の配列を取り出す。右のウィンドウの遺伝子をクリックするか、左のウィンドウで検索する。ここではDnaAと検索。

片方はDnaA遺伝子ではなく、DnaAに関連するタンパク質をコードする遺伝子だった。DnaA遺伝子の方をクリックする。下のウィンドウにDnaA遺伝子の配列が表示された。

赤いのがDnaA遺伝子の塩基配列。周辺にコードされている遺伝子も表示されている。
下にはタンパク質配列も表示されている。

他のORFをダブルクリックすると、そのORFの配列に切り替わる。

サイズは変更できる。30kbに変更。

この30kbの配列をすべてダウンロードするならFull sequenceをクリックする。DNA配列がfasta 形式でダウンロードされる。
- 提供されたゲノム情報は、サーバーによってロードされ、RAMで完全に処理される。
- ユーザーデータは単一のユーザーセッションに制限されており、同時セッション間で共有されることはない。
- すべてのユーザーデータは、セッションの終了時にメモリから完全に削除される。処理中に管理者がアクセスできることもない。
- BAGETは、選択された遺伝子のアクセッション/バージョンを用いて、NCBIリポジトリへの直接外部リンクを提供している。
- BAGETは、選択された遺伝子のアクセッション/バージョンを用いて、Uniprotのウェブサイトへの直接外部リンクを提供している。
PDFレポート機能もあるが、試した時は動作しなかった。
引用
BAGET 2.0: an updated web tool for the effortless retrieval of prokaryotic gene context and sequence
Benjamin Hepp, Violette Da Cunha, Florence Lorieux, Jacques Oberto
Bioinformatics, Published: 03 February 2021