2018 9/22 タイトル修正
BRIG(BLAST Ring Image Generator)はゲノム比較のためのツール。blast(blastn、blastp、blastxなど選択可能)を行い、ホモロジー解析結果をリング状の図に出力することができる。ゲノムサイズは20Mまで対応しているらしい。javaのGUIプログラムなので、javaとblastさえインストールされていれば特別なコマンド知識がなくても利用できる。
http://brig.sourceforge.net/brig-tutorial-1-whole-genome-comparisons/
ダウンロード
https://sourceforge.net/projects/brig/
マニュアルPDFも同封されている。
本体 Github
ラン
オーサーらが準備したexampleデータを解析してみる(リンク)。
ダウンロードしたファイルを解凍しておく。

BRIG.jarをダブルクリックして起動する。

一番上のReferenceには、BRIG_examples/Chapter5_6_8_wholeGenomeExamples/BRIGExample.fnaを選択。
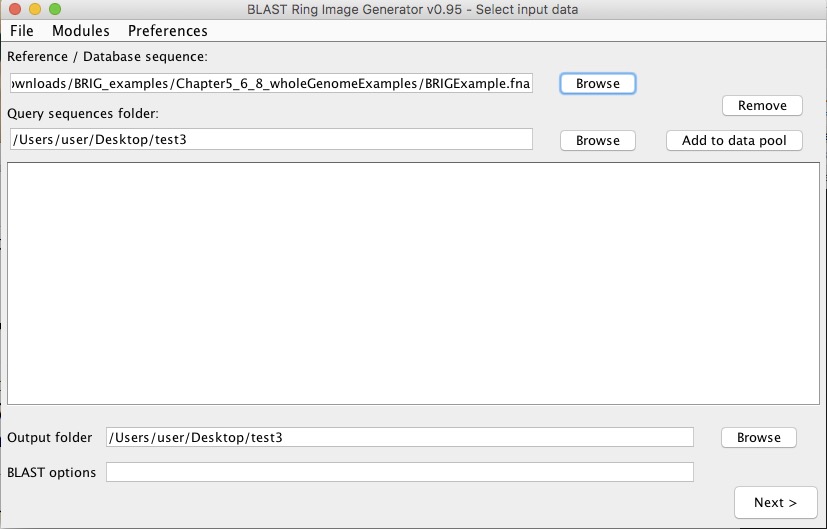
Referenceには、prokkaなどでアノテーションして得たgenbankファイルを指定する事も出来る。
続いて、Query folderでは、BRIGが認識可能なfaa、fasta、gbk、graphなどのファイルが配置されているフォルダを指定する。
Query folderにBRIG_examples/Chapter5_6_8_wholeGenomeExamples/を選択。

右上のAdd to data poolボタンをクリックしてフォルダ内容を追加。
OutputはBRIG_examples/にした。BLASTは空白でO.K。Nextをクリック。
Insert new ringをクリックして、描画したいデータ分だけリングを追加する(GC plotも1つのリングとみなされる)。RING1が一番内側となる。

Legend textは"GC content"とする。
真ん中のウィンドウのGC Contentを選択し、その下のAdd dataボタンを押す。これでring1にはGC contentが割り振られた。同様に、ring2-6にもデータを追加する。1つのリングに複数のゲノムなどアサイン出来てしまうが、2つ以上アサインすると次の描画で計算が停止する。
マニュアル通り指定する。

最終的にこうした。

PreferenceからBRIG optionsを選択。

defaultだと出力に余白がないので、HeightとWidthを2800くらいまで上げておく。

Save & closeをクリックし、さらにNextをクリック。
出力フォルダとファイル名を指定する。/Users/user/Downloads/BRIG_examples/outputとした。

Submitする。

2800x2800だといい感じで余白ができます。
追記; 複数のクロモソームには対応していないようです。1つ1つ比較する必要があります。
引用
BLAST Ring Image Generator (BRIG): simple prokaryote genome comparisons
Nabil-Fareed Alikhan,1 Nicola K Petty,1 Nouri L Ben Zakour,1 and Scott A Beatson
BMC Genomics. 2011; 12: 402.
関連
おすすめ