Serial Clonerは、MacintoshとWindowsに対応した遺伝子編集ソフトウェア。 FASTAファイルの読み書き、DNA Striderと互換性のあるファイルの読み書きをサポートする。 Vector NTI、MacVector、ApE、DNAstar、pDRAW32およびGenBank形式、さらにVectorNTIマルチファイル形式で保存されたファイルもインポート可能になっている。 強力なグラフィカル表示ツールと簡単なインターフェイスで、無料で誰でも簡単に使うことができる(Paypalで寄付が可能です)。
PDFマニュアル
http://serialbasics.free.fr/Serial_Cloner-Download_files/SerialCloner-User%20Manual%20%28v1-2%29.pdf
簡単な紹介
http://dibernardo.tigem.it/internal-site/files/menolascina/tutorial-sc.pdf
公式ページ
SerialCloner2-6-1 installerをダウンロードし、指示に従ってインストールする。
Serial Clonerを立ち上げ、newをクリックするとウィンドウが出現する。
 解析したい配列をコピー&ペーストする。
解析したい配列をコピー&ペーストする。
またはオープンから配列のファイルを選択する。
配列を編集するにはロックのチェックを外す。

上のSequenceのメニューから、逆相補鎖、リバース、小文字、大文字などに変換できる。

変換したい部分をマウスで囲んでから実行する。小文字にした。
Site usageを選択すると、制限酵素の消化回数が示される。uniqueのチェックだけにすると、その配列に対してユニークな制限酵素の一覧を確認できる。

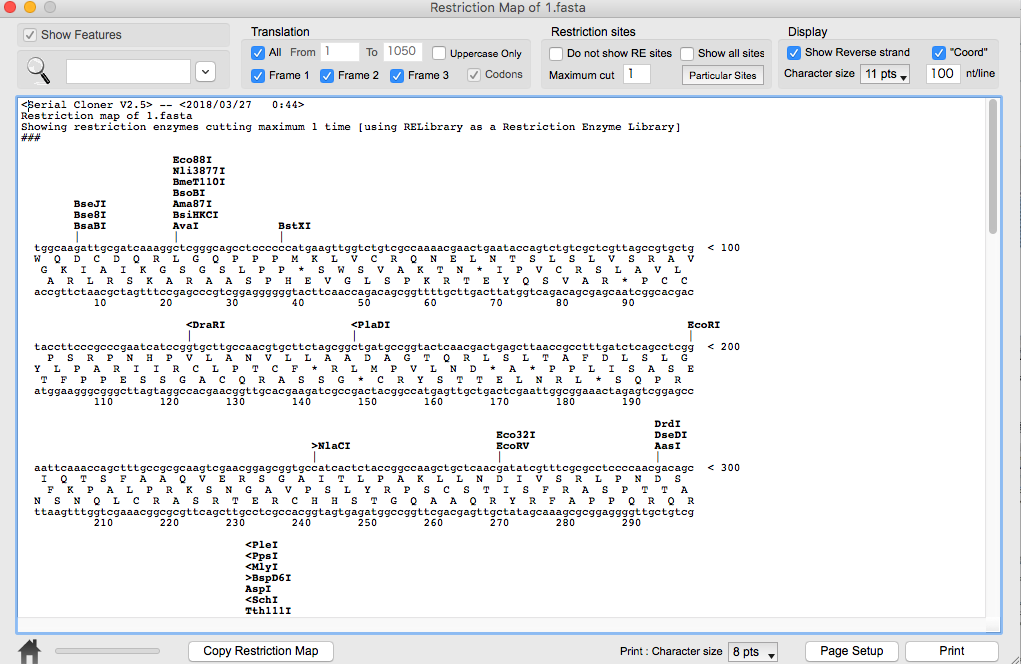
SequenceからCircularをクリックし、制限酵素マップを表示する。上のGraphic mapを選択。

環状で制限酵素部位がグラフィック表示された。
上のSite usageを選択すると、各制限酵素サイトの数が一覧表示される。
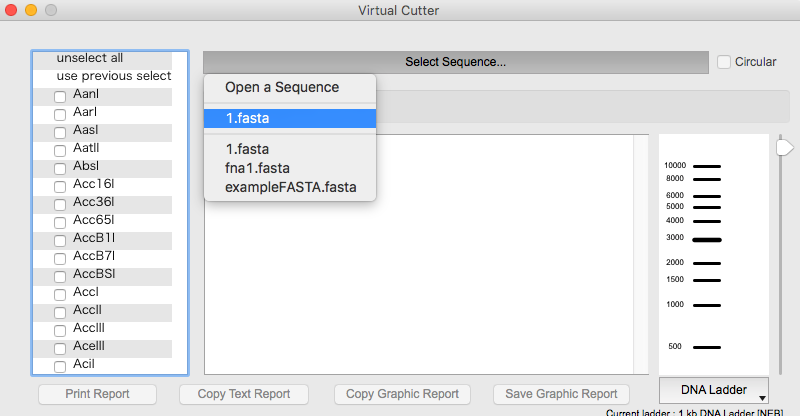
その右隣りのVirtual cutterを選択すると、指定した制限酵素処理後の電気泳動のバンドパターンをシミュレートできる。まず配列を選択する。環状DNAなら右のチェックもつける。
制限酵素を1つ選択すると、バンドが1つだけ表示された(1カ所だけで切れて線状DNAになった時の泳動サイズ)。

もう一つ選ぶと、もう1ヶ所で切れるため、バンドが2つ表示された。左下からプリントして起き、実験で同じ結果が得られるか確認する。

制限酵素リストを絞りたければ、Restriction => enzyme libraryから選ぶ。
Alignを選択すれば、2つの配列をアライメントできる(search homology)。

上のFindから、100%合致する配列を検索できる。また右端のORFsから推定コード領域を表示できる。
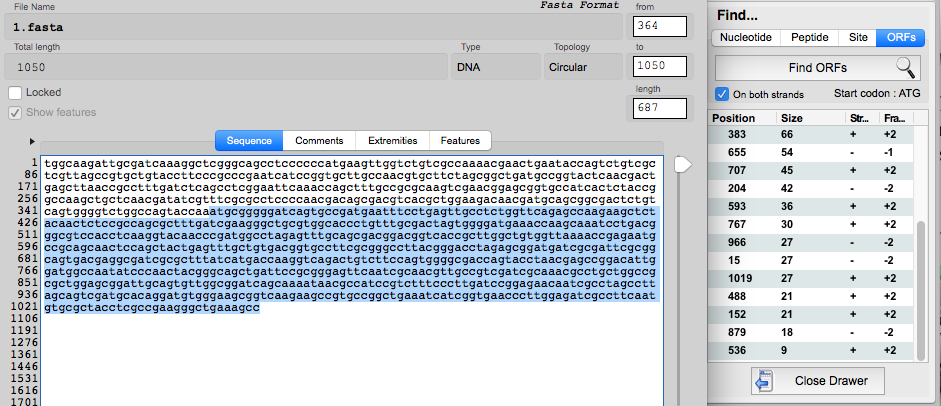
プラスミドをダウンロードし、アノテーションをつけてみる。
Cloning vector pUC-JK, complete sequence - Nucleotide - NCBI

右上から選択すれば、fastaファイルがダウンロードできる。
Serial Clonerで開いて、ScanをクリックすればFeatureが検出される。circularにしてからGraphic mapを表示。

公式から動画マニュアルもアップされている。
Subcloning
Feature manipulation
引用
